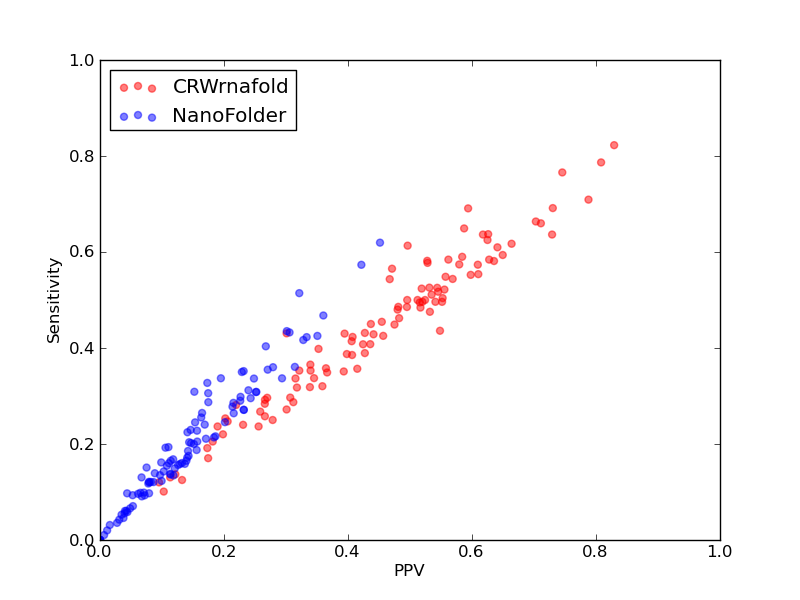
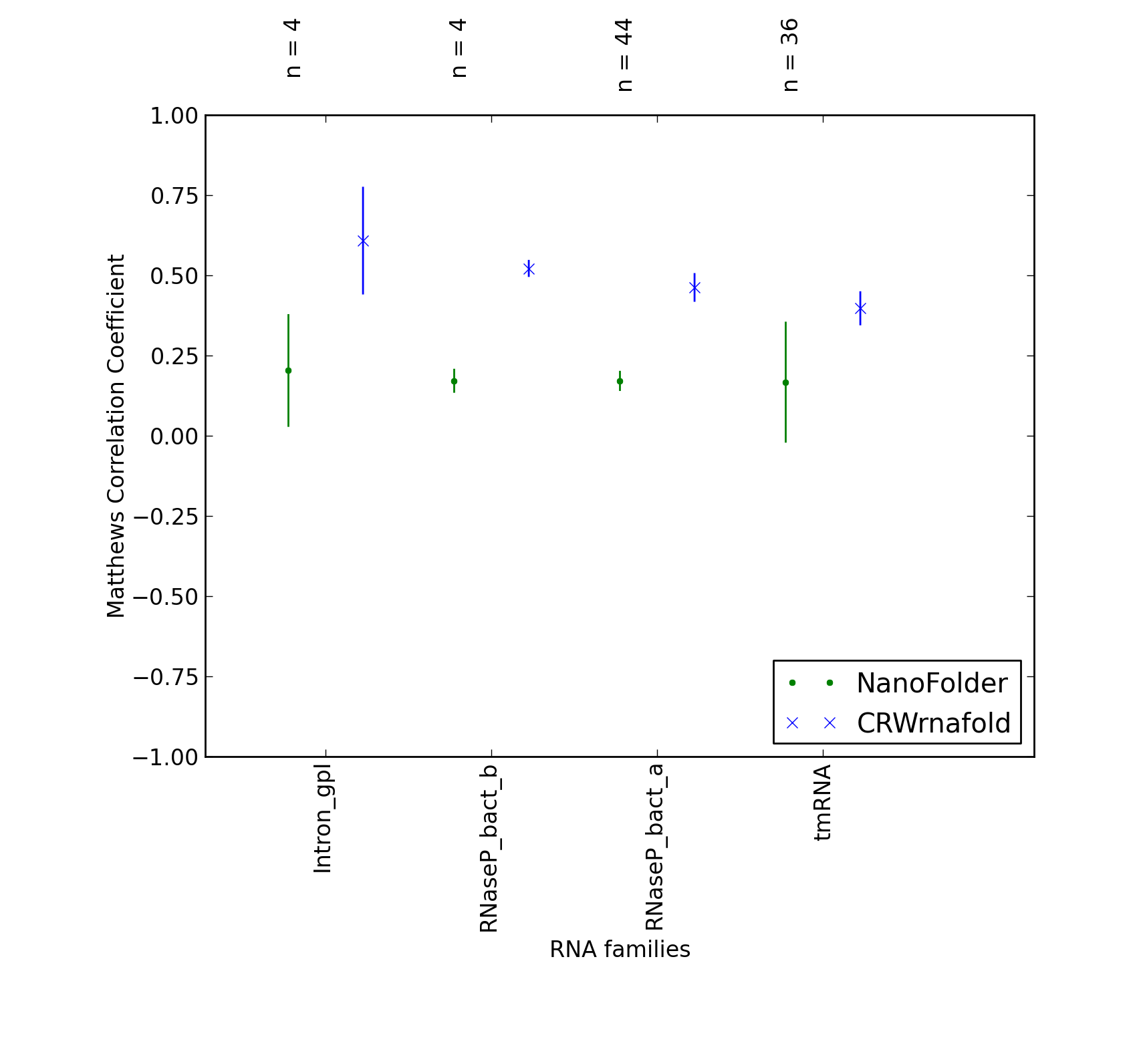
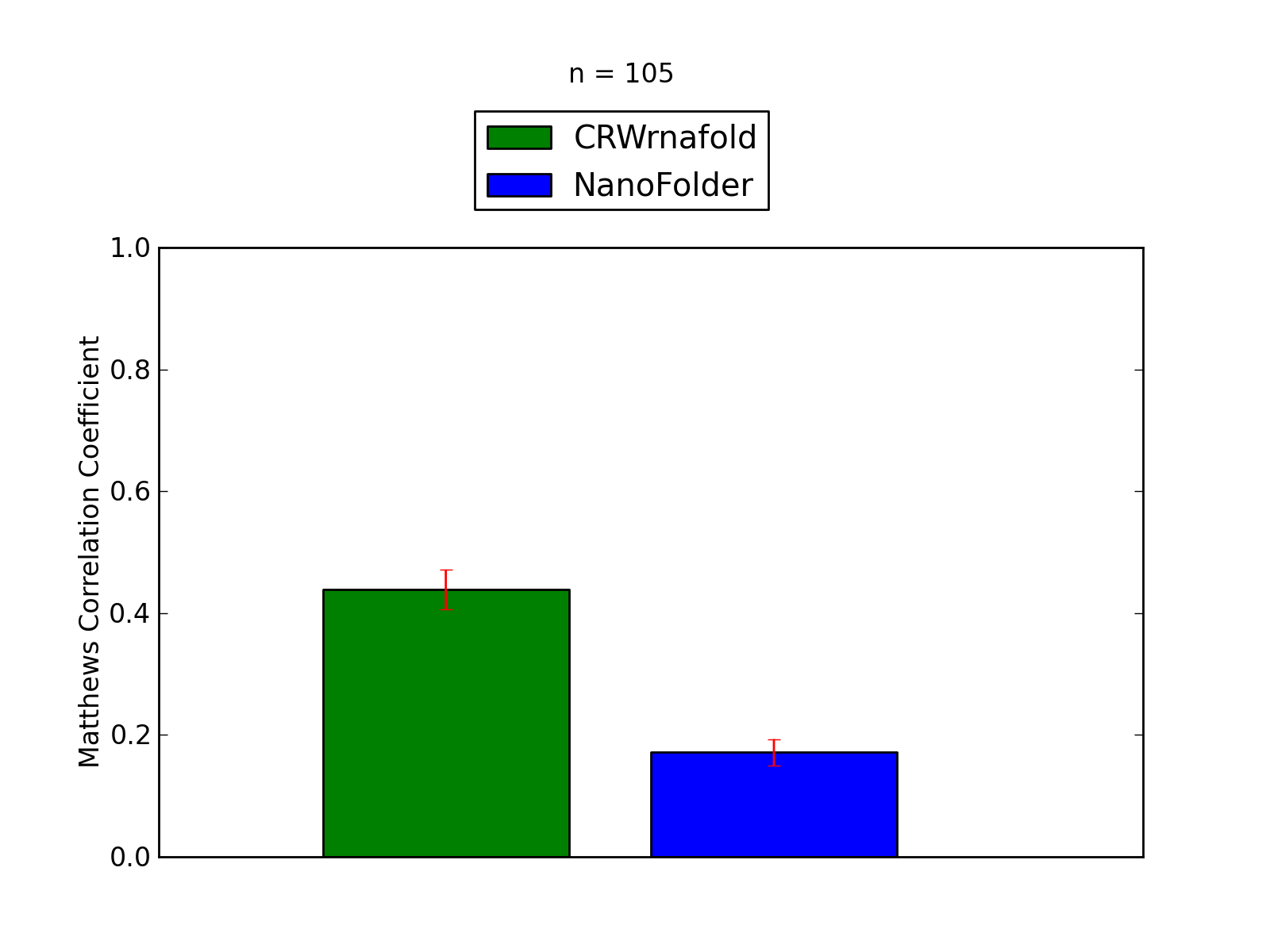
| ASE_00017 |
RNaseP_nuc
links to Rfam database...
|
0.02 |
0.03 |
0.02 |
2 |
50914 |
131 |
38 |
86 |
7 |
62 |
| ASE_00083 |
RNaseP_bact_a
links to Rfam database...
|
0.22 |
0.25 |
0.20 |
27 |
62347 |
108 |
12 |
95 |
1 |
83 |
| ASE_00122 |
RNaseP_bact_a
links to Rfam database...
|
0.27 |
0.30 |
0.24 |
26 |
43258 |
84 |
13 |
68 |
3 |
62 |
| ASE_00185 |
RNaseP_bact_a
links to Rfam database...
|
0.17 |
0.19 |
0.16 |
24 |
73382 |
134 |
14 |
116 |
4 |
104 |
| ASE_00190 |
RNaseP_bact_b
links to Rfam database...
|
0.24 |
0.28 |
0.21 |
25 |
45334 |
93 |
14 |
78 |
1 |
65 |
| ASE_00196 |
RNaseP_arch
links to Rfam database...
|
0.49 |
0.57 |
0.42 |
43 |
31524 |
62 |
16 |
43 |
3 |
32 |
| ASE_00221 |
RNaseP_bact_a
links to Rfam database...
|
0.20 |
0.21 |
0.18 |
25 |
64484 |
112 |
10 |
101 |
1 |
92 |
| ASE_00227 |
RNaseP_bact_a
links to Rfam database...
|
0.28 |
0.31 |
0.25 |
41 |
78840 |
122 |
20 |
102 |
0 |
92 |
| ASE_00228 |
RNaseP_bact_a
links to Rfam database...
|
0.05 |
0.06 |
0.04 |
5 |
46858 |
109 |
17 |
91 |
1 |
81 |
| ASE_00229 |
RNaseP_bact_a
links to Rfam database...
|
0.12 |
0.14 |
0.11 |
12 |
42380 |
97 |
12 |
82 |
3 |
75 |
| ASE_00231 |
RNaseP_bact_a
links to Rfam database...
|
0.37 |
0.42 |
0.33 |
40 |
47773 |
84 |
17 |
65 |
2 |
56 |
| ASE_00234 |
RNaseP_bact_a
links to Rfam database...
|
0.25 |
0.27 |
0.23 |
35 |
75315 |
117 |
10 |
106 |
1 |
94 |
| ASE_00238 |
RNaseP_bact_a
links to Rfam database...
|
0.26 |
0.30 |
0.23 |
34 |
64111 |
119 |
18 |
98 |
3 |
80 |
| ASE_00248 |
RNaseP_bact_a
links to Rfam database...
|
0.13 |
0.15 |
0.12 |
17 |
62340 |
124 |
9 |
115 |
0 |
97 |
| ASE_00250 |
RNaseP_bact_a
links to Rfam database...
|
0.25 |
0.29 |
0.23 |
38 |
78835 |
135 |
17 |
113 |
5 |
93 |
| ASE_00254 |
RNaseP_bact_a
links to Rfam database...
|
0.15 |
0.16 |
0.14 |
13 |
36761 |
88 |
3 |
79 |
6 |
69 |
| ASE_00255 |
RNaseP_bact_a
links to Rfam database...
|
0.11 |
0.12 |
0.10 |
16 |
74530 |
146 |
16 |
129 |
1 |
114 |
| ASE_00257 |
RNaseP_bact_a
links to Rfam database...
|
0.37 |
0.42 |
0.33 |
41 |
50917 |
85 |
15 |
67 |
3 |
56 |
| ASE_00267 |
RNaseP_bact_a
links to Rfam database...
|
0.00 |
0.00 |
0.00 |
0 |
45036 |
115 |
9 |
105 |
1 |
88 |
| ASE_00270 |
RNaseP_bact_a
links to Rfam database...
|
0.19 |
0.21 |
0.17 |
27 |
72232 |
132 |
14 |
117 |
1 |
101 |
| ASE_00274 |
RNaseP_bact_a
links to Rfam database...
|
0.00 |
0.00 |
0.00 |
0 |
55487 |
126 |
12 |
112 |
2 |
103 |
| ASE_00277 |
RNaseP_bact_a
links to Rfam database...
|
0.10 |
0.12 |
0.08 |
11 |
48071 |
123 |
23 |
100 |
0 |
80 |
| ASE_00279 |
RNaseP_bact_a
links to Rfam database...
|
0.14 |
0.16 |
0.13 |
16 |
53177 |
109 |
16 |
92 |
1 |
85 |
| ASE_00285 |
RNaseP_bact_a
links to Rfam database...
|
0.34 |
0.36 |
0.31 |
44 |
68866 |
98 |
14 |
82 |
2 |
78 |
| ASE_00287 |
RNaseP_bact_a
links to Rfam database...
|
0.15 |
0.17 |
0.14 |
17 |
54824 |
107 |
14 |
91 |
2 |
86 |
| ASE_00294 |
RNaseP_bact_a
links to Rfam database...
|
0.12 |
0.13 |
0.12 |
23 |
114287 |
172 |
11 |
160 |
1 |
148 |
| ASE_00295 |
RNaseP_bact_a
links to Rfam database...
|
0.14 |
0.16 |
0.13 |
21 |
73761 |
140 |
19 |
119 |
2 |
110 |
| ASE_00298 |
RNaseP_bact_a
links to Rfam database...
|
0.09 |
0.10 |
0.08 |
11 |
67389 |
129 |
8 |
120 |
1 |
102 |
| ASE_00318 |
RNaseP_bact_b
links to Rfam database...
|
0.03 |
0.04 |
0.03 |
5 |
80039 |
156 |
21 |
135 |
0 |
113 |
| ASE_00335 |
RNaseP_bact_b
links to Rfam database...
|
0.10 |
0.12 |
0.09 |
14 |
75304 |
151 |
22 |
126 |
3 |
102 |
| ASE_00339 |
RNaseP_bact_a
links to Rfam database...
|
0.25 |
0.29 |
0.22 |
34 |
80042 |
129 |
20 |
104 |
5 |
85 |
| ASE_00340 |
RNaseP_bact_a
links to Rfam database...
|
0.06 |
0.07 |
0.05 |
6 |
45943 |
110 |
13 |
94 |
3 |
79 |
| ASE_00343 |
RNaseP_bact_a
links to Rfam database...
|
0.14 |
0.17 |
0.12 |
19 |
83275 |
145 |
31 |
111 |
3 |
94 |
| ASE_00367 |
RNaseP_bact_a
links to Rfam database...
|
0.08 |
0.09 |
0.07 |
8 |
42960 |
110 |
10 |
93 |
7 |
78 |
| ASE_00370 |
RNaseP_bact_a
links to Rfam database...
|
0.03 |
0.04 |
0.03 |
3 |
41796 |
109 |
18 |
88 |
3 |
81 |
| ASE_00372 |
RNaseP_bact_a
links to Rfam database...
|
0.17 |
0.20 |
0.15 |
20 |
51871 |
113 |
19 |
93 |
1 |
80 |
| ASE_00375 |
RNaseP_bact_a
links to Rfam database...
|
0.12 |
0.14 |
0.11 |
15 |
60246 |
120 |
10 |
107 |
3 |
95 |
| ASE_00376 |
RNaseP_bact_a
links to Rfam database...
|
0.00 |
0.00 |
0.00 |
0 |
56822 |
136 |
9 |
122 |
5 |
105 |
| ASE_00377 |
RNaseP_bact_a
links to Rfam database...
|
0.25 |
0.27 |
0.23 |
29 |
57505 |
98 |
10 |
86 |
2 |
78 |
| ASE_00386 |
RNaseP_bact_a
links to Rfam database...
|
0.14 |
0.16 |
0.13 |
15 |
50284 |
106 |
9 |
95 |
2 |
81 |
| ASE_00393 |
RNaseP_bact_a
links to Rfam database...
|
0.31 |
0.35 |
0.27 |
33 |
47773 |
90 |
18 |
71 |
1 |
60 |
| ASE_00412 |
RNaseP_bact_a
links to Rfam database...
|
0.15 |
0.17 |
0.14 |
18 |
58183 |
111 |
14 |
96 |
1 |
87 |
| ASE_00413 |
RNaseP_bact_a
links to Rfam database...
|
0.08 |
0.10 |
0.07 |
8 |
44438 |
108 |
19 |
86 |
3 |
73 |
| ASE_00416 |
RNaseP_bact_a
links to Rfam database...
|
0.39 |
0.43 |
0.35 |
54 |
77267 |
103 |
18 |
82 |
3 |
73 |
| ASE_00417 |
RNaseP_arch
links to Rfam database...
|
0.32 |
0.36 |
0.28 |
36 |
54486 |
98 |
18 |
75 |
5 |
64 |
| ASE_00422 |
RNaseP_bact_a
links to Rfam database...
|
0.28 |
0.31 |
0.25 |
29 |
46856 |
87 |
9 |
77 |
1 |
65 |
| ASE_00428 |
RNaseP_bact_a
links to Rfam database...
|
0.24 |
0.26 |
0.22 |
33 |
76483 |
121 |
13 |
107 |
1 |
92 |
| ASE_00429 |
-
|
0.08 |
0.09 |
0.07 |
6 |
28114 |
84 |
14 |
69 |
1 |
60 |
| ASE_00430 |
RNaseP_bact_a
links to Rfam database...
|
0.16 |
0.18 |
0.14 |
17 |
46852 |
102 |
10 |
92 |
0 |
80 |
| ASE_00434 |
RNaseP_bact_b
links to Rfam database...
|
0.29 |
0.34 |
0.25 |
37 |
68116 |
122 |
20 |
92 |
10 |
73 |
| ASE_00437 |
RNaseP_bact_a
links to Rfam database...
|
0.00 |
0.00 |
0.00 |
0 |
79238 |
164 |
12 |
151 |
1 |
135 |
| ASE_00451 |
RNaseP_bact_a
links to Rfam database...
|
0.20 |
0.22 |
0.19 |
27 |
70731 |
118 |
8 |
110 |
0 |
98 |
| CRW_00648 |
-
|
0.05 |
0.06 |
0.04 |
9 |
137864 |
213 |
24 |
178 |
11 |
139 |
| CRW_00654 |
-
|
0.41 |
0.47 |
0.36 |
58 |
78049 |
105 |
18 |
85 |
2 |
66 |
| CRW_00658 |
-
|
0.21 |
0.26 |
0.16 |
27 |
74527 |
137 |
28 |
109 |
0 |
75 |
| CRW_00663 |
-
|
0.08 |
0.10 |
0.07 |
6 |
26014 |
90 |
17 |
69 |
4 |
55 |
| CRW_00664 |
-
|
0.14 |
0.19 |
0.11 |
15 |
53486 |
134 |
42 |
85 |
7 |
63 |
| CRW_00671 |
Intron_gpI
links to Rfam database...
|
0.18 |
0.21 |
0.16 |
24 |
62682 |
130 |
23 |
106 |
1 |
93 |
| CRW_00672 |
Intron_gpI
links to Rfam database...
|
0.36 |
0.43 |
0.31 |
48 |
72233 |
114 |
35 |
74 |
5 |
63 |
| CRW_00674 |
Intron_gpI
links to Rfam database...
|
0.16 |
0.19 |
0.14 |
23 |
83274 |
142 |
19 |
120 |
3 |
101 |
| CRW_00676 |
Intron_gpI
links to Rfam database...
|
0.11 |
0.14 |
0.09 |
16 |
93347 |
169 |
29 |
136 |
4 |
99 |
| CRW_00685 |
-
|
0.11 |
0.15 |
0.08 |
16 |
156867 |
212 |
64 |
133 |
15 |
90 |
| CRW_00688 |
-
|
0.33 |
0.40 |
0.27 |
23 |
21859 |
64 |
21 |
42 |
1 |
34 |
| CRW_00721 |
-
|
0.22 |
0.31 |
0.15 |
21 |
58515 |
133 |
46 |
71 |
16 |
47 |
| PDB_00078 |
-
|
0.00 |
0.00 |
0.00 |
0 |
49644 |
126 |
10 |
116 |
0 |
115 |
| PDB_00278 |
-
|
0.04 |
0.06 |
0.04 |
4 |
24875 |
98 |
13 |
84 |
1 |
68 |
| PDB_00701 |
-
|
0.04 |
0.05 |
0.04 |
5 |
45319 |
127 |
14 |
113 |
0 |
104 |
| PDB_00917 |
-
|
0.31 |
0.34 |
0.29 |
32 |
35136 |
81 |
10 |
67 |
4 |
63 |
| TMR_00036 |
tmRNA
links to Rfam database...
|
0.22 |
0.29 |
0.17 |
29 |
90359 |
153 |
37 |
100 |
16 |
72 |
| TMR_00123 |
tmRNA
links to Rfam database...
|
0.19 |
0.23 |
0.16 |
23 |
66283 |
126 |
20 |
104 |
2 |
78 |
| TMR_00180 |
tmRNA
links to Rfam database...
|
0.12 |
0.16 |
0.10 |
16 |
66999 |
149 |
35 |
111 |
3 |
83 |
| TMR_00240 |
tmRNA
links to Rfam database...
|
0.23 |
0.31 |
0.17 |
26 |
63041 |
128 |
39 |
84 |
5 |
59 |
| TMR_00352 |
tmRNA
links to Rfam database...
|
0.07 |
0.09 |
0.05 |
7 |
95133 |
171 |
39 |
87 |
45 |
68 |
| TMR_00353 |
tmRNA
links to Rfam database...
|
0.41 |
0.51 |
0.32 |
54 |
84087 |
127 |
49 |
65 |
13 |
51 |
| TMR_00357 |
tmRNA
links to Rfam database...
|
0.26 |
0.34 |
0.19 |
31 |
82869 |
146 |
44 |
84 |
18 |
61 |
| TMR_00361 |
-
|
0.06 |
0.10 |
0.04 |
7 |
93368 |
174 |
64 |
89 |
21 |
65 |
| TMR_00374 |
tmRNA
links to Rfam database...
|
0.09 |
0.13 |
0.07 |
12 |
81631 |
174 |
44 |
123 |
7 |
80 |
| TMR_00384 |
tmRNA
links to Rfam database...
|
0.17 |
0.20 |
0.14 |
22 |
65550 |
133 |
26 |
105 |
2 |
86 |
| TMR_00395 |
tmRNA
links to Rfam database...
|
0.27 |
0.31 |
0.24 |
34 |
64478 |
115 |
10 |
98 |
7 |
75 |
| TMR_00398 |
tmRNA
links to Rfam database...
|
0.05 |
0.07 |
0.05 |
7 |
65197 |
139 |
24 |
113 |
2 |
99 |
| TMR_00399 |
tmRNA
links to Rfam database...
|
0.20 |
0.26 |
0.16 |
24 |
64833 |
130 |
38 |
85 |
7 |
70 |
| TMR_00430 |
tmRNA
links to Rfam database...
|
0.18 |
0.23 |
0.15 |
25 |
82450 |
148 |
34 |
112 |
2 |
84 |
| TMR_00431 |
tmRNA
links to Rfam database...
|
0.24 |
0.33 |
0.17 |
18 |
51899 |
127 |
26 |
60 |
41 |
37 |
| TMR_00443 |
tmRNA
links to Rfam database...
|
0.17 |
0.20 |
0.15 |
21 |
67018 |
126 |
24 |
98 |
4 |
83 |
| TMR_00457 |
tmRNA
links to Rfam database...
|
0.19 |
0.25 |
0.15 |
25 |
78443 |
141 |
39 |
99 |
3 |
77 |
| TMR_00469 |
tmRNA
links to Rfam database...
|
0.10 |
0.12 |
0.08 |
12 |
64469 |
145 |
27 |
112 |
6 |
88 |
| TMR_00502 |
tmRNA
links to Rfam database...
|
0.14 |
0.19 |
0.11 |
18 |
75303 |
150 |
45 |
100 |
5 |
75 |
| TMR_00503 |
tmRNA
links to Rfam database...
|
0.11 |
0.14 |
0.10 |
15 |
67741 |
141 |
20 |
120 |
1 |
96 |
| TMR_00519 |
tmRNA
links to Rfam database...
|
0.04 |
0.05 |
0.03 |
5 |
63046 |
141 |
33 |
106 |
2 |
90 |
| TMR_00528 |
tmRNA
links to Rfam database...
|
0.13 |
0.15 |
0.11 |
15 |
63051 |
131 |
20 |
104 |
7 |
82 |
| TMR_00541 |
tmRNA
links to Rfam database...
|
0.12 |
0.14 |
0.10 |
15 |
61630 |
139 |
22 |
109 |
8 |
90 |
| TMR_00547 |
tmRNA
links to Rfam database...
|
0.28 |
0.35 |
0.23 |
35 |
65188 |
122 |
37 |
81 |
4 |
65 |
| TMR_00562 |
tmRNA
links to Rfam database...
|
0.09 |
0.12 |
0.08 |
12 |
72617 |
147 |
27 |
115 |
5 |
90 |
| TMR_00566 |
tmRNA
links to Rfam database...
|
0.13 |
0.16 |
0.11 |
16 |
60582 |
132 |
22 |
106 |
4 |
84 |
| TMR_00571 |
tmRNA
links to Rfam database...
|
0.05 |
0.06 |
0.04 |
6 |
60577 |
149 |
19 |
124 |
6 |
93 |
| TMR_00584 |
tmRNA
links to Rfam database...
|
0.01 |
0.01 |
0.01 |
1 |
60922 |
159 |
33 |
119 |
7 |
96 |
| TMR_00594 |
tmRNA
links to Rfam database...
|
0.08 |
0.10 |
0.06 |
10 |
79238 |
156 |
30 |
123 |
3 |
94 |
| TMR_00605 |
tmRNA
links to Rfam database...
|
0.28 |
0.35 |
0.23 |
38 |
74141 |
129 |
36 |
90 |
3 |
70 |
| TMR_00609 |
tmRNA
links to Rfam database...
|
0.53 |
0.62 |
0.45 |
70 |
63391 |
89 |
28 |
57 |
4 |
43 |
| TMR_00624 |
tmRNA
links to Rfam database...
|
0.36 |
0.44 |
0.30 |
47 |
62325 |
111 |
27 |
82 |
2 |
61 |
| TMR_00683 |
tmRNA
links to Rfam database...
|
0.01 |
0.02 |
0.01 |
2 |
82854 |
176 |
50 |
122 |
4 |
98 |
| TMR_00698 |
tmRNA
links to Rfam database...
|
0.20 |
0.24 |
0.17 |
25 |
63042 |
124 |
27 |
96 |
1 |
79 |
| TMR_00703 |
tmRNA
links to Rfam database...
|
0.10 |
0.12 |
0.08 |
12 |
67376 |
140 |
26 |
114 |
0 |
87 |
| TMR_00706 |
tmRNA
links to Rfam database...
|
0.14 |
0.17 |
0.11 |
17 |
66281 |
133 |
29 |
103 |
1 |
86 |
| TMR_00711 |
tmRNA
links to Rfam database...
|
0.18 |
0.22 |
0.14 |
22 |
67740 |
137 |
41 |
93 |
3 |
76 |